Phycodnaviridae
Die Phycodnaviren, wissenschaftlich Phycodnaviridae (von griechisch φῦκος phŷkos „(See-)Tang“, „(Rot-)Algen“ und DNA), bilden eine Familie großer Doppelstrang-DNA-Viren mit einem Genom von 160 bis 560 Kb. Sie infizieren Meeres- und Süßwasser-Algen und gehören zu einem Phylum großer Viren, das vom International Committee on Taxonomy of Viruses (ICTV) im März als Nucleocytoviricota (veraltet Nucleocytoplasmaviricota oder Nucleocytoplasmic large DNA viruses, NCLDV) offiziell bestätigt wurde.
| Phycodnaviridae | ||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|

Bild (Negativ) von Micromonas pusilla virus SP1, | ||||||||||||||
| Systematik | ||||||||||||||
| ||||||||||||||
| Taxonomische Merkmale | ||||||||||||||
| ||||||||||||||
| Wissenschaftlicher Name | ||||||||||||||
| Phycodnaviridae | ||||||||||||||
| Links | ||||||||||||||
|
Struktur und Vermehrung
Phycodnaviren haben eine icosahedrale Gestalt, eine interne Doppellipidschicht und sie vermehren sich im Cytoplasma der Wirtszelle.
Molekularbiologische Besonderheiten
Jüngste Untersuchungen der Phycodnavirus-Genome haben bei diesen Viren ausgeklügelte Mechanismen der Virus-DNA Replikation und Transkriptions-Vorgänge gefunden. Ebenfalls wurde ein neuer Typ von Kaliumkanälen entdeckt. Es wurden auch Gene gefunden, die an der Apoptose der Wirtszelle sowie an den komplexen Signalpfaden, Transkritpionsmechanismen und für die Glykosylierung viraler Proteine beteiligt sind. Alle Phycodnaviren haben Gene, die für DNA-Polymerasen codieren. Dennoch ist bislang nicht klar, ob Phycodnaviren einen kompletten Replikations-Komplex herstellen können. Wahrscheinlich benötigen sie für die Replikation die Unterstützung der Wirtszelle.
Systematik
Äußere Systematik
In älteren Arbeiten findet sich noch die Bezeichnungsweise Megavirales (vom Rang einer Ordnung), vom Umfang her entweder für das gesamte Phylum NCLDV oder nur für die gemeinsame Klasse (jetzt Megaviricetes) mit der Ordnung Imitervirles der Familie Mimiviridae. Diese Bezeichnungen sind mit der Master Species List #35 des ICTV vom März 2020 überholt.
Innere Systematik
Zu den Phycodnaviren gehören laut ICTV mit Stand November 2018 offiziell folgende Gattungen:[3]
- Phycodnaviridae
- Chlorovirus mit Paramecium bursaria Chlorella virus 1 (PBCV-1), Acanthocystis turfacea chlorella virus 1 (ATCV-1),…
- Coccolithovirus mit Emiliania huxleyi virus 86 (EhV-86)[4]
- Phaeovirus mit Ectocarpus siliculosus virus 1 (EsV-1), Feldmannia species virus (FsV), …
- Prasinovirus mit Micromonas pusilla virus SP1 (MpV-SP1) und Ostreococcus tauri virus OtV5 (OTV5)
- Prymnesiovirus mit Chrysochromulina brevifilum virus PW1 (CbV-PW1)
- Raphidovirus mit Heterosigma akashiwo virus 01 (HaV01, auch HaV-01, unterscheide: Heterosigma akashiwo RNA virus – HaRNAV und Heterosigma akashiwo nuclear inclusion virus − HaNIV)[5][6][7][8]
- Als weitere vom ICTV (noch) nicht bestätigte Spezies der Phycodnaviridae wurden vorgeschlagen:[9]
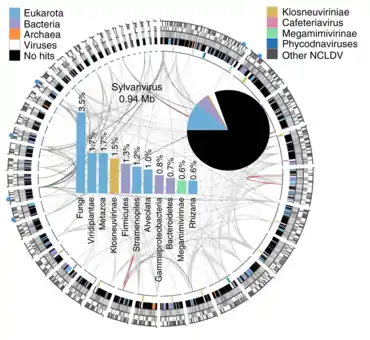
- „Sylvanvirus“[10]
- „Yellowstone Lake Phycodnaviruses“ (YSLPV)[11]
offenbar gelegentlich als Yellow Lake Phycodnavirus (YLPV) fehlgeschrieben[10][12] - „Dishui Lake Phycodnavirus 1“ (DSLPV1)[11][14] bis „Dishui Lake Phycodnavirus 4“ (DSLPV4).[15][Anm. 2] Fundort: Dishui Lake 30,8972° N, 121,9353° O, ein künstlich angelegter See in der Modellstadt Nanhui New City, Pudong, Schanghai.
- „Clandestinovirus ST1“ und „Usurpativirus LCD7“[16]
- „Micromonas pusilla virus 02T“ (MpV-02T)
- „Micromonas pusilla virus 04T“ (MpV-02T)
- „Micromonas pusilla virus 05T“ (MpV-02T)
- „Micromonas pusilla virus 07T“ (MpV-02T)
- „Micromonas pusilla virus 13T“ (MpV-02T)
- „Micromonas pusilla virus 38T“ (MpV-02T)
- „Micromonas pusilla virus 40T“ (MpV-02T)
- „Micromonas pusilla virus 41T“ (MpV-02T)
- „Micromonas virus MiV93“ (MiV93)
- „Micromonas virus MiV100“ (MiV100)
- „Micromonas virus MiV130“ (MiV130)
Kladogramm (Schulz)
Die folgende Systematik folgt F. Schulz et al. (2018) und Hao Chen et al. (2018):[10][Anm. 3] Das Kladogramm wurde ergänzt um die neuen Kandidaten aus dem Dushui Lake nach Shengzhong Xu et al. (2020):[15]
| Phycodnaviridae |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
BpV = „Bathycoccus prasinos virus“
DSLPV = „Dishui Lake Phycodnavirus“
MpV = „Micromonas pusilla virus“
YSLPV = „Yellowstone Lake Phycodnavirus“
Greiner et al. (2018) sehen YLPV2 (alias YSLPV2, Yellowstone Phycodnavirus 2) jedoch nicht in der Klade der Viren vom Chlorovirus-Typ.[18]
Kladogramm (Koonin)
Koonin et al. (2019) und Rolland et al. (2019) stellen einen im Vergleich dazu etwas modifizieren Stammbaum dar,[2][16] in den sich aber die Dishui-Lake-Phycodnaviren nach Xu (2020)[15] ebenfalls integrirern lassen:
| Phycodnaviridae |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
In diesem Kladogramm sind Raphidovirus und die Usurpativirus-Klade berücksichtigt, es fehlt dagegen „Sylvanvirus“.[Anm. 4][19]
Zusammenfassung
Den Vorschlägen gemeinsam ist, dass „Mollivirus“ und die Pandoraviren eine gemeinsame Klade weiterentwickelter Abkömmlinge der Phycodnaviren darstellen. Ein Unterschied besteht lediglich in der Stellung diese relativ zu den Coccolitho- und Phaeoviren. Bei Koonin et al. (2019) hat die Gruppe der Pandoraviren einen gemeinsamen Vorfahren mit den Coccolithoviren innerhalb der Familie Phycodnaviridae.[20] Übereinstimmend sind auch die Coccolithoviren genetisch nur weitläufig mit der gemeinsamen Klade aus Chlorovirus und Prasinovirus verwandt, was nach Koonin et al. (2019) auch für Raphidovirus gilt.
Die vom ICTV im März 2020 neu geschaffene Ordnung Algavirales könnte möglicherweise eine gemeinsame Heimat all dieser Kandidaten werden, den Hauptgruppenkäme dann der Rang eigenständiger Familien zu.
Umgruppierungen
Die Gattungen Prymnesiovirus und Rapidovirus sind nicht dargestellt: Nach neueren Untersuchungen sind einige früher für Phycodnaviridae gehaltene Kandidaten eher den Mimiviridae nahestehend, würden also in die vom ICTV neu geschaffene Ordnung Imitervirales (erweiterte Mimiviridae) innerhalb der gemeinsamen Klasse Megaviricetes mit den Phycodnaviridae fallen. Insbesondere gilt dies für die Gruppe der Organic Lake Phycodnaviruses („OLPG“) um die Gattung Organic Lake Phycodnavirus (OLPV),[11][Anm. 2] für die vorgeschlagen wurde, sie als Unterfamilie Mesomimivirinae zu einer so erweiterten Familie Mimiviridae zuzuordnen.
Von dieser Umgruppierung betroffen sind u. a.
- vermutlich innerhalb der OLPG:
- Organic Lake Phycodnavirus 1 und 2 (OLPV1, OLPV2)
- Phaeocystis globosa virus 12, 14, 16 (PgV-12T, PgV-14T, PgV-16T)[21] – PgV-16T gehört definitiv einer anderen Virusgruppe an als PgV-01T (Gattung Prymnesiovirus)[22]
- Phaeocystis pouchetii virus (PpV),[23][24]
- Yellowstone Lake Phycodnavirus 4 (YSLPV4) alias Yellowstone lake giant virus (YSLGV) oder Yellowstone lake mimivirus[25][Anm. 2][26][27][Anm. 5][26]
- Prymnesium kappa virus RF01 und RF02 (PkV-RF01, PkV-RF02)[28][29][30]
- Chrysochromulina ericina virus 01 (CeV, alias Haptolina ericina virus)[31][26][30]
- vermutlich außerhalb der OLPG:
- Aureococcus anophagefferens virus (AaV)[32]
- Tetraselmis virus (TetV-1)
- Pyramimonas orientalis virus 01 (PoV)[8]
Möglicherweise ist auch die Gattung Raphidovirus (zumindest der Vertreter Heterosigma akashiwo virus strain HaV53) nicht bei den Phycodnaviridae, sondern in einer eigenen Klade, eventuell zusammen mit Aureococcus anophagefferens virus anzusiedeln,[33][5] etwa zusammen mit der vorgeschlagenen Gattung „Choanovirus“.
Für die gesamte Gruppe der betroffenen Kandidaten wurde ursprünglich der Rang einer Unterfamilie namens Mesomimivirinae innerhalb einer erweiterten Familie Mimiviridae vorgeschlagen.[22][34] Neuere Vorschläge erheben diese Gruppe in den Rang einer Familie Mesomoimiviridae, die damit ein Schwestertaxon der Mimiviridae innerhalb der neuen Ordnung Imitervirales (tritt an die Stelle der erweiterten Mimiviridae) wäre.
Literatur
- J. L. Van Etten: Unusual life style of giant chlorella viruses. In: Annu Rev Genet. 37, 2003, S. 153–195. Review. PMID 14616059. (Open Access version)
- J. L. Van Etten, R. H. Meints: Giant viruses infecting algae. In: Annu Rev Microbiol. 53, 1999, S. 447–494. Review. PMID 10547698. (Open Access version)
- L. M. Iyer, S. Balaji, E. V. Koonin, L. Aravind: Evolutionary genomics of nucleo-cytoplasmic large DNA viruses. In: Virus Research. 117(1), Apr 2006, S. 156–184. PMID 16494962
- D. Raoult, S. Audic, C. Robert, C. Abergel, P. Renesto, H. Ogata, B. La Scola, M. Suzan, J. M. Claverie: The 1.2-megabase genome sequence of Mimivirus. In: Science. 306(5700), 19. November 2004, S. 1344–1350. doi:10.1126/science.1101485 PMID 15486256
- Fumito Maruyama, Shoko Ueki: Evolution and Phylogeny of Large DNA Viruses, Mimiviridae and Phycodnaviridae Including Newly Characterized Heterosigma akashiwo Virus. In: Front. Microbiol., 30. November 2016, doi:10.3389/fmicb.2016.01942
- Jean-Michel Claverie: Challenges in classifying newly discovered viruses (cf. giant viruses) (PDF; 1,2 MB) Structural & Genomic Information Laboratory (IGS), Mediterranean Institute of Microbiology (IMM), CNRS - Aix-Marseille University
- Natalya Yutin, Eugene V Koonin: Pandoraviruses are highly derived phycodnaviruses. In: Biology Direct 2013 8:25, doi:10.1186/1745-6150-8-25
Weblinks
- Viralzone: Phycodnaviridae
- World of Chlorella Viruses Home Page
- Willie Wilson, James L Van Etten, D. S. Schroeder, Keizo Nagasaki et al.: Family: Phycodnaviridae, 8th ICTV Report, auf: Elsevier/Academic Press, Januar 2005, S. 163–175;
- Curtis A Suttle, Amy M Chan: Family: Phycodnaviridae, 9th ICTV Report, auf: Elsevier/Academic Press, Januar 2011, S. 1269–1273, doi:10.1007/978-0-387-95919-1_207
Anmerkungen
- Das Material wurde von dieser Quelle kopiert, die unter einer Creative Commons Attribution 4.0 International License verfügbar ist.
-
Unterscheide Phycodnaviren (ggf. möglicherweise Mesomimivirinae) und ihre Virophagen:
- Yellowstone Lake Phycodnavirus(YSLPV) und Yellowstone Lake giant virus (YSLGV, Mimiviridae) versus Yellowstone Lake Virophages (YSLVs)
- Dishui Lake Phycodnavirus (DSLPV) versus Dishui Lake Virophages (DSLVs)
- Organic Lake Phycodnavirus (OLPV) versus Organic Lake Virophages (OLVs)
- Qinghai Lake Virophage QLV
- Die Gattungen Prymnesiovirus (mit Spezies Chrysochromulina brevifilum virus PW1, CbV-PW1) und Raphidovirus (mit Spezies Heterosigma akashiwo virus 01, HaV01) sind in diesen Arbeiten nicht berücksichtigt, Phaevirus bei Schulz et al. (2018) ist als Phaeovirus zu lesen. YLPV ist offenbar als YSLPV zu verstehen, denn die Schreibweise Yellow Lake Phycodnavirus (Ylpv-A, Ylpv-B) findet sich sonst nur bei Kinyanyi et al. (2018). Nach Hao Chen et al. (2018) Fig. 2b muss damit YSLPV1 und YSLPV2 gemeint sein. Zur Klärung siehe auch Zhang et al. (2015).
- Die von den Autoren angegebenen Speziesnamen sind zur Vereinfachung durch die zugehörigen Gattungen ersetzt. Für die hier informell (ad hoc) bezeichneten Kladen bieten sich von anderen Autoren bereits früher verwendete Unterfamilien-Bezeichnungen, etwa „Chlorovirinae“ alias Phycodnaviruses s. l. (Koonin) und „Coccolithovirinae“ an, siehe Allen et al. (2006).
- Unterscheide vorschlagsgemäße Yellowstone Lake Virophages (YSLVs) sowie das nicht verwandte, nicht weiter klassifizierte Yellowstone hot spring archaeal RNA virus (species)
Einzelnachweise
- ICTV: ICTV Master Species List 2019.v1, New MSL including all taxa updates since the 2018b release, March 2020 (MSL #35)
- Eugene V. Koonin, Natalya Yutin: Evolution of the Large Nucleocytoplasmatic DNA Viruses of Eukaryotes and Convergent Origins of Viral Gigantism. In: Advances in Virus research, Band 103, AP 21. Januar 2019, doi:10.1016/bs.aivir.2018.09.002, S. 167–202. In Fig. 4 ist phycodnaviruses wohl im engeren Sinne (s. s.) zu verstehen und dürfte der Chlorovirus/Prasinovirus/‚YLPV‘-Gruppe bei Schulz et al. (2018) entsprechen.
- ICTV: Master Species List 2018a v1, MSL #33 including all taxa updates since the 2017 release. (Herbst 2018).
- Graziele Oliveira, Bernard La Scola, Jônatas Abrahão: Giant virus vs amoeba: fight for supremacy. In: Virol J, 16, 126, 4. November 2019, doi:10.1186/s12985-019-1244-3, researchgate.net (PDF).
- Fumito Maruyama, Shoko Ueki: Evolution and Phylogeny of Large DNA Viruses, Mimiviridae and Phycodnaviridae Including Newly Characterized Heterosigma akashiwo Virus. In: Frontiers in Microbiology. 7, 30. November 2016, S. 1942. doi:10.3389/fmicb.2016.01942. PMID 27965659. PMC 5127864 (freier Volltext).
- Yuji Tomaru, Yoko Shirai, Keizo Nagasaki: Ecology, physiology and genetics of a phycodnavirus infecting the noxious bloom-forming raphidophyte Heterosigma akashiwo. In: Fisheries Science. 74, Nr. 4, 1. August 2008, ISSN 1444-2906, S. 701–711. doi:10.1111/j.1444-2906.2008.01580.x.
- Keizo Nagasaki, Kenji Tarutani, Mineo Yamaguchi: Growth Characteristics of Heterosigma akashiwo Virus and Its Possible Use as a Microbiological Agent for Red Tide Control. In: Applied and Environmental Microbiology. 65, Nr. 3, 1. März 1999, ISSN 0099-2240, S. 898–902. PMID 10049839. PMC 91120 (freier Volltext).
- Christopher R. Schvarcz, Grieg F. Steward: A giant virus infecting green algae encodes key fermentation genes. In: Virology, Band 518, Mai 2018, S. 423–433, doi:10.1016/j.virol.2018.03.010
- NCBI: unclassified Phycodnaviridae (list)
- Frederik Schulz, Lauren Alteio, Danielle Goudeau, Elizabeth M. Ryan, Feiqiao B. Yu, Rex R. Malmstrom, Jeffrey Blanchard, Tanja Woyke: Hidden diversity of soil giant viruses. In: Nature Communications, volume 9, Article number: 4881, 19. November 2018, doi:10.1038/s41467-018-07335-2
- Hao Chen, Weijia Zhang, Xiefei Li, Yingjie Pan, Shuling Yan, Yongjie Wang: The genome of a prasinoviruses-related freshwater virus reveals unusual diversity of phycodnaviruses, in: BMC Genomics, Dezember 2018, 19:49 (online 15. Januar 2018), doi:10.1186/s12864-018-4432-4: Yellowstone Lake phycodnavirus (YSLPV, Phycodnaviridae) versus Yellowstone lake giant virus (YSLGV, Mimiviridae); daneben DSLPV1 (Phycodnaviridae)
- Dickson Kinyanyi, George Obiero, Peris W Amwayi, Stephen Mwaniki, Mark Wamalwa: In silico structural and functional prediction of African swine fever virus protein-B263R reveals features of a TATA-binding protein. In: PeerJ 6(4):e4396 (2018), doi:10.7717/peerj.4396, S. 13, insbes. Fig. 7 (Ylpv-A, Ylpv-B)
- Julien Andreani, Jacques Y. B. Khalil, Emeline Baptiste, Issam Hasni, Caroline Michelle, Didier Raoult, Anthony Levasseur, Bernard La Scola: Orpheovirus IHUMI-LCC2: A New Virus among the Giant Viruses. In: Front. Microbiol., 22. Januar 2018, doi:10.3389/fmicb.2017.02643
- NCBI: Dishui lake phycodnavirus 1 (species).
- Shengzhong Xu, Liang Zhou, Xiaosha Liang, Yifan Zhou, Hao Chen, Shuling Yan, Yongjie Wang; Julie K. Pfeiffer (Hrsg.): Novel Cell-Virus-Virophage Tripartite Infection Systems Discovered in the Freshwater Lake Dishui Lake in Shanghai, China. In: Journal of Virology, 18. Mai 2020, doi:10.1128/JVI.00149-20, PMID 32188734.
- Clara Rolland, Julien Andreani, Amina Cherif Louazani, Sarah Aherfi, Rania Francis, Rodrigo Rodrigues, Ludmila Santos Silva, Dehia Sahmi, Said Mougari, Nisrine Chelkha, Meriem Bekliz, Lorena Silva, Felipe Assis, Fábio Dornas, Jacques Yaacoub Bou Khalil, Isabelle Pagnier, Christelle Desnues, Anthony Levasseur, Philippe Colson, Jônatas Abrahão, Bernard La Scola: Discovery and Further Studies on Giant Viruses at the IHU Mediterranee Infection That Modified the Perception of the Virosphere. In: Viruses, 11(4), März/April 2019, pii: E312, doi:10.3390/v11040312, PMC 6520786 (freier Volltext), PMID 30935049, MDPI, Fig. 2a
- Eugene V. Koonin, Natalya Yutin: Multiple evolutionary origins of giant viruses. In: F1000 Research. 22. November 2018, doi:10.12688/f1000research.16248.1, version 1.
- Timo Greiner, Anna Moroni, James L. Van Etten, Gerhard Thiel: Genes for Membrane Transport Proteins: Not So Rare in Viruses. In: MDPI Viruses, Band 10, Nr. 9, Special Issue Algae Virus, 26 August 2018, 456; doi:10.3390/v10090456
- Michael J. Allen, Declan C. Schroeder, Matthew T. G. Holden, William H. Wilson: Evolutionary History of the Coccolithoviridae. In: Molecular Biology and Evolution, Volume 23, Issue 1, 1. Januar 2006, S. 86–92, doi:10.1093/molbev/msj010
- Natalya Yutin, Eugene V. Koonin: Pandoraviruses are highly derived phycodnaviruses. In: Biology Direct. 8, Oktober 2013, S. 25. doi:10.1186/1745-6150-8-25. PMID 24148757.
- Jônatas Abrahão, Lorena Silva, Ludmila Santos Silva, Jacques Yaacoub Bou Khalil, Rodrigo Rodrigues, Thalita Arantes, Felipe Assis, Paulo Boratto, Miguel Andrade, Erna Geessien Kroon, Bergmann Ribeiro, Ivan Bergier, Herve Seligmann, Eric Ghigo, Philippe Colson, Anthony Levasseur, Guido Kroemer, Didier Raoult, Bernard La Scola: Tailed giant Tupanvirus possesses the most complete translational apparatus of the known virosphere. In: Nature Communications. 9, Nr. 1, 27. Februar 2018. doi:10.1038/s41467-018-03168-1.
- Jean-Michel Claverie, Chantal Abergel: Mimiviridae: An Expanding Family of Highly Diverse Large dsDNA Viruses Infecting a Wide Phylogenetic Range of Aquatic Eukaryotes. In: Viruses. 2018 Sep; 10(9), 18. September 2018, S. 506, doi:10.3390/v10090506, PMC 6163669 (freier Volltext), PMID 30231528
- NCBI: Phaeocystis pouchetii virus (species).
- Natalya Yutin, Philippe Colson, Didier Raoult, Eugene V Koonin: Mimiviridae: clusters of orthologous genes, reconstruction of gene repertoire evolution and proposed expansion of the giant virus family, in: Virol J. 2013; 10: 106, 4. April 2013, doi:10.1186/1743-422X-10-106, PMC 3620924 (freier Volltext), PMID 23557328.
- Weijia Zhang, Jinglie Zhou, Taigang Liu, Yongxin Yu, Yingjie Pan, Shuling Yan, Yongjie Wang: Four novel algal virus genomes discovered from Yellowstone Lake metagenomes. In: Scientific Reports, volume 5, Artikel Nr. 15131, 2015, doi:10.1038/srep15131
- Sailen Barik: A Family of Novel Cyclophilins, Conserved in the Mimivirus Genus of the Giant DNA Viruses. In: Computational and Structural Biotechnology Journal, Band 16, Juli 2018, S. 231–236, doi:10.1016/j.csbj.2018.07.001.
- NCBI: Yellowstone lake mimivirus (species)
- NCBI: Prymnesium kappa virus (species).
- Lucie Gallot-Lavallee, Guillaume Blanc, Jean-Michel Claverie: Comparative genomics of Chrysochromulina Ericina Virus (CeV) and other microalgae-infecting large DNA viruses highlight their intricate evolutionary relationship with the established Mimiviridae family. (PDF) In: J. Virol., 26 April 2017, doi:10.1128/JVI.00230-17.
- Torill Vik Johannessen, Gunnar Bratbak, Aud Larsenb, Hiroyuki Ogatac, Elianne S.Egged, Bente Edvardsen, Wenche Eikremd, Ruth-Anne Sandaaa: Characterisation of three novel giant viruses reveals huge diversity among viruses infecting Prymnesiales (Haptophyta). In: Virology, Band 476, Februar 2015, S. 180–188, doi:10.1016/j.virol.2014.12.014, PMID 25546253.
- List of the main “giant” viruses known as of today (PDF; 334 kB) Centre National de la Recherche Scientifique, Université Aix Marseille, vom 18. April 2018.
- Mohammad Moniruzzaman, Alaina R. Weinheimer, Carolina A. Martinez-Gutierrez, Frank O. Aylward: Widespread endogenization of giant viruses shapes genomes of green algae. In: nature, 18. November 2020, doi:10.1038/s41586-020-2924-2, dazu:
Kendall Daniels: Lurking in genomic shadows: How giant viruses fuel the evolution of algae, vtnews, SciTechDaily, Quelle: Virginia Tech, 18. November 2020. - Yoshitoshi Ogura, Tetsuya Hayashi, Shoko Ueki: Complete Genome Sequence of a Phycodnavirus, Heterosigma akashiwo Virus Strain 53. In: Microbiology, September 2016, doi:10.1128/genomeA.01279-16, PMID 27834719, mra.asm.org (PDF)
- Carolina Reyes, Kenneth Stedman: Are Phaeocystis globosa viruses (OLPG) and Organic Lake phycodnavirus a part of the Phycodnaviridae or Mimiviridae?, Blog auf ResearchGate, 8. Januar 2016.