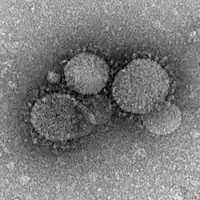
Betacoronavirus
Betacoronaviren sind eine von vier Gattungen von Coronaviren der Unterfamilie Orthocoronavirinae in der Familie Coronaviridae der Ordnung Nidovirales. In der älteren Literatur wird diese Gattung auch als Gruppe-2-Coronaviren bezeichnet. Es sind umhüllte einzelsträngige RNA-Viren mit positiver Polarität und zoonotischem Ursprung.
| Betacoronavirus | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ||||||||||||||||||||
| Systematik | ||||||||||||||||||||
| ||||||||||||||||||||
| Taxonomische Merkmale | ||||||||||||||||||||
| ||||||||||||||||||||
| Wissenschaftlicher Name | ||||||||||||||||||||
| Betacoronavirus | ||||||||||||||||||||
| Kurzbezeichnung | ||||||||||||||||||||
| Beta-CoV, BetaCoV | ||||||||||||||||||||
| Links | ||||||||||||||||||||
|
Die Coronavirus-Gattungen setzen sich jeweils aus verschiedenen viralen „Linien“ (englisch lineage ‚Abstammungslinie‘) zusammen, wobei die Gattung Betacoronavirus vier solcher Linien enthält (Stand 2001), die mittlerweile als vier Untergattungen plus eine weitere Untergattung klassifiziert werden.[3] Neben Alphacoronavirus sind sie die einzige Gattung, die in Fledermausarten gefunden wurde (Stand 2019).[4]
Die Typusart der Gattung ist Murine coronavirus (dt. Maus-Coronavirus),[5] zu der etwa die Unterart Ratten-Coronavirus gehört. Die Betacoronaviren mit der größten klinischen Bedeutung für den Menschen sind das Humane Coronavirus OC43 und das Humane Coronavirus HKU1 der A-Linie (Untergattung Embecovirus), SARS-CoV-1[6] und SARS-CoV-2 (alias 2019-nCoV) der B-Linie (Untergattung Sarbecovirus) und MERS-CoV der C-Linie (Untergattung Merbecovirus).
Vorkommen
Im Hinblick auf die Evolution der Coronaviren lässt sich zeigen, dass die Gattungen Alphacoronavirus und Betacoronavirus aus dem Genpool von Fledermäusen stammen. Vertreter beider Gattungen sind in der Lage, den Menschen zu infizieren.[7][8][9]
Fledermausarten aus der Familie der Glattnasen (Vespertilionidae) sind Wirtstiere von Betacoronaviren,[3] beispielsweise die folgenden Arten:[3][10]
- Zwergfledermaus (Pipistrellus pipistrellus) und Pipistrellus abramus aus der Gattung Zwergfledermäuse (Pipistrellus),
- Alpenfledermaus (Hypsugo savii, Synonym: Pipistrellus savii) aus der Gattung Hypsugo,
- Eptesicus isabellinus aus der Gattung Breitflügelfledermäuse (Eptesicus) und
- Tylonycteris pachypus aus der Gattung Bambusfledermäuse (Tylonycteris).
Außerdem:
- Stoliczka-Dreizackblattnase (Aselliscus stoliczkanus) aus der Familie der Rundblattnasen (Hipposideridae).[11]
Arten aus der Familie der Hufeisennasen (Rhinolophidae) sind ebenfalls Wirtstiere für Betacoronaviren,[3] beispielsweise die folgenden Arten[10][12]
- Rhinolophus ferrumequinum (Große Hufeisennase),
- Rhinolophus macrotis (Großohr-Hufeisennase),
- Rhinolophus pearsonii (Pearson-Hufeisennase),
- Rhinolophus sinicus (Chinesische Hufeisennase) – Virenspezies SARS-assoziiertes Coronavirus – und
- Rhinolophus affinis (Java-Hufeisennase, englisch intermediate horseshoe bat)[13][14][6] – Virenspezies SARS-assoziiertes Coronavirus.
Weitere Wirtstiere von Betacoronaviren sind unter den Säugetieren u. a.:[9][10]
- Virenspezies Betacoronavirus 1:
- Virenspezies Severe acute respiratory syndrome-related coronavirus:
- Larvenroller (Larvenroller-SARS-Coronavirus PC4-13 [Civet-SARS-CoV-PC4-13] und Larvenroller-SARS-Coronavirus SZ3 [Civet-SARS-CoV-SZ3]),
- Schuppentiere (Schuppentier-Coronavirus [Manis-CoV])[15]
- Virenspezies Murine coronavirus:
- Altweltmäuse (Murines Hepatitis-Virus [MHV]),
- Ratten (Ratten-Coronavirus [RtCoV]).
Wirtstiere anderer Wirbeltier-Klassen sind nachweislich:
- Virenspezies Murine coronavirus:
- Vögel (Puffinosis coronavirus [PV], bei Schwarzschnabel-Sturmtauchern der Art Atlantiksturmtaucher, wissenschaftlich Puffinus puffinus)
Molekulargenetik
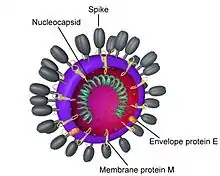
Das einzelsträngige RNA-Genom der Betacoronaviren ist etwa 29.000 bis 31.100 Nukleotide (nt) lang.[10] Die komplette RNA-Sequenzanalyse mittels Reverse-Transkriptase-Polymerase-Kettenreaktion (RT-PCR) von drei bei Fledermäusen isolierten Betacoronaviren (HKU4, HKU5 und HKU9) ergibt eine Genomgröße von 29.017 bis 30.488 Nukleotiden, der GC-Gehalt (der Anteil der Nukleinbasen Guanin und Cytosin) liegt zwischen 38 und 41 Mol-Prozent. Die Reihenfolge der Gene entspricht weitgehend der von anderen Coronaviren: Am 5′-Ende finden sich die beiden Offenen Leserahmen ORF 1a und ORF 1b, die den größten Teil des Genoms (20.800 bis 21.000 nt) ausmachen und für die Nichtstrukturproteine (NSP) 1a und 1b codieren. Dann folgen die Gene, die für die Hämagglutinin-Esterase (HE), die Spikes (S), Virushülle (E für englisch envelope ‚Hülle‘), Matrixproteine (M) und Nukleokapsid (N) codieren. Sowohl am 5′-Ende wie am 3′-Ende finden sich kurze, nichtcodierende Regionen (UTR, engl. untranslated region). Das HE-Gen kommt nur bei den Betacoronaviren vor.[8]
Die Offenen Leserahmen (ORF) codieren für mehrere putative (vermutete) Proteine, darunter
- NSP 3 (enthält die putative Papain-ähnliche Protease PLPro),
- NSP 5 (enthält die putative Chymotrypsin-ähnliche Protease 3CLPro),
- NSP 12 (enthält die putative RNA-abhängige RNA-Polymerase, engl. RNA-dependent RNA polymerase RdRP),
- NSP 13 (enthält die putative Helikase),
- NSP 14 (enthält die putative 3′→5′-Exonuklease ExoN),
- NSP 15 (enthält die putative poly(U)-spezifische Endoribonuklease XendoU) und
- NSP 16 (enthält die putative S-Adenosylmethionin-abhängige 2'-O-Ribose-Methyltransferase 2'-O-MT).
Dabei entstehen die Nichtstrukturproteine durch spezifische proteolytische Spaltung durch die PLPro und 3CLPro aus einem zunächst erzeugten Replikase-Polyprotein 1ab.[8]
Da Betacoronaviren verschiedenen Wirte haben und Teile ihres Genoms rekombiniert werden, stellen sie eine potentielle Gefahr für die menschliche Gesundheit dar. So zeigte ein genetischer Vergleich eines im Jahr 2012 aus menschlichem Sputum isolierten Betacoronvirus mit Beta-CoV, die bei Fledermäusen auftreten, eine Übereinstimmung der Nukleotidsequenzen von 82,0 % – 87,7 %.[3]
Systematik
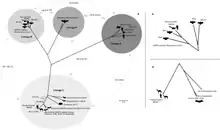
| Kladogramm basierend auf der phylogenetischen Analyse der Virus-Genome von repräsentativen Virus-Isolaten der Gattung Betacoronavirus (Stand 2020) | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Der obere Teil der Klade 3 ist aufgrund der Vorlagen-Beschränkung vereinfacht. Zur Virustaxonomie: englisch bat ‚Fledermaus‘; SARS-related coronavirus (englisch) = SARS-assoziiertes Coronavirus (dt.) = SARS-like coronavirus (englisch) = SARS virus (englisch) = SARS coronavirus (englisch), es handelt sich jeweils um heterotypische Synonyme;[16] SARS = Severe acute respiratory syndrome (englisch) = Schweres Akutes Atemwegssyndrom (dt.); die Angabe der Jahreszahl in der Klammer bezieht sich auf die Veröffentlichung der Genomanalysen, sie sind in der NCBI GenBank abrufbar. nach R. Lu et al. (2020)[17], ergänzende Angaben nach J. F.-W. Chan et al. (2020)[18] |
Innerhalb der Gattung Betacoronavirus (früher als Gruppe-2-Coronaviren bezeichnet) wurden durch phylogenetische Untersuchungen vier Untergruppen (engl. lineage ‚Abstammungslinie‘) identifiziert, die mit Buchstaben (A, B, C und D bzw. a, b, c und d), griechischen Buchstaben (α, β, γ und δ) und manchmal auch mit Zahlen gekennzeichnet werden.[3][8] Im Jahr 2018 wurden diese Untergruppen als Untergattungen klassifiziert, sowie eine fünfte Untergattung (Subgenus) Hibecovirus definiert.[19][20]
- Lineage A → Subgenus Embecovirus
- Lineage B → Subgenus Sarbecovirus
- Lineage C → Subgenus Merbecovirus
- Lineage D → Subgenus Nobecovirus
- Subgenus Hibecovirus
Durch die zunehmende Anzahl von Genomanalysen, die in Datenbanken veröffentlicht werden, ist es möglich, eine phylogenetische Systematik zu erstellen. Im Zusammenhang mit dem Auftreten des „neuartigen Coronavirus von 2019“ (2019-nCoV, neuere Bezeichnung: SARS-CoV-2) haben mehrere Gruppen von Wissenschaftlern die Ergebnisse ihrer phylogenetischen Untersuchungen veröffentlicht. Die evolutionären Beziehungen zwischen den Vertretern der Betacoronaviren werden dabei auch als phylogenetischer Baum veranschaulicht,[17][18] darauf basiert die Darstellung in diesem Artikel. Die Genomsequenzen sind unter anderem in der GenBank des Nationalen Zentrums für Biotechnologieinformation (NCBI) verfügbar.[21]
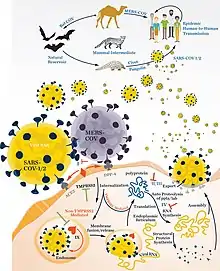
Medizinische Bedeutung
Mehrere Vertreter der Gattung Betacoronavirus sind in der Lage, den Menschen zu infizieren.[7][9] Beta-CoV, die an Epidemien beteiligt waren, verursachen oftmals Fieber und Atemwegsinfektionen. Bekannte Beispiele sind:
- SARS-CoV-1,[6] verursacht das schwere akute Atemwegssyndrom (severe acute respiratory syndrome, SARS), zuerst 2002 in China aufgetreten (SARS-Pandemie 2002/2003)
- MERS-CoV („Middle East respiratory syndrome coronavirus“), mehrere Epidemien ab 2012
- SARS-CoV-2 (vormals „2019-nCoV“, „neuartiges Coronavirus von 2019“), COVID-19-Pandemie
Einzelnachweise
- ICTV Taxonomy history: Betacoronavirus, ICTV Master Species List 2018b, MSL #34. Februar 2019, abgerufen am 1. Februar 2020.
- ICTV: ICTV Taxonomy history: Severe acute respiratory syndrome-related coronavirus, EC 51, Berlin, Germany, July 2019; Email ratification March 2020 (MSL #35)
- Matthew Cotten, Tommy T. Lam, Simon J. Watson, Anne L. Palser, Velislava Petrova, Paul Grant, Oliver G. Pybus, Andrew Rambaut, Y. i. Guan, Deenan Pillay, Paul Kellam, Eleni Nastouli: Full-Genome Deep Sequencing and Phylogenetic Analysis of Novel Human Betacoronavirus. In: Emerging Infectious Diseases. Band 19, Nr. 5, Mai 2013, S. 736–742, doi:10.3201/eid1905.130057, PMID 23693015, PMC 3647518 (freier Volltext).
- Antonio C. P. Wong, Xin Li, Susanna K. P. Lau and Patrick C. Y. Woo: Global Epidemiology of Bat Coronaviruses. Abstract. In: Viruses. Volume, Nr. 11. MDPI, 20. Februar 2019, S. 174, doi:10.3390/v11020174, PMID 30791586, PMC 6409556 (freier Volltext) – (englisch, Volltext [PDF; 2,2 MB; abgerufen am 31. Mai 2020]).
- ICTV: ICTV Master Species List 2019.v1. MSL #35, März 2020
- Kristian G. Andersen, Andrew Rambaut, W. Ian Lipkin, Edward C. Holmes, Robert F. Garry: The Proximal Origin of SARS-CoV-2. In: virologica.org, Quelle: ARTIC Network, 17. Februar 2020
- Patrick C. Y. Woo, Susanna K. P. Lau: Viruses and Bats. In: Viruses. Band 11, Nr. 10, Oktober 2019, S. 884, doi:10.3390/v11100884, PMID 31546572, PMC 6832948 (freier Volltext).
- P. C. Y. Woo, M. Wang, S. K. P. Lau, H. Xu, R. W. S. Poon, R. Guo, B. H. L. Wong, K. Gao, H.-w. Tsoi, Y. Huang, K. S. M. Li, C. S. F. Lam, K.-h. Chan, B.-j. Zheng, K.-y. Yuen: Comparative Analysis of Twelve Genomes of Three Novel Group 2c and Group 2d Coronaviruses Reveals Unique Group and Subgroup Features. In: Journal of Virology. Band 81, Nr. 4, Februar 2007, S. 1574–1585, doi:10.1128/JVI.02182-06, PMID 17121802, PMC 1797546 (freier Volltext).
- TRBA (Technische Regeln für Biologische Arbeitsstoffe) 462: Einstufung von Viren in Risikogruppen. In: Website der Bundesanstalt für Arbeitsschutz und Arbeitsmedizin (BAuA). 25. April 2012, S. 23–24, abgerufen am 1. Februar 2020 (letzte Änderung vom 3. Juli 2018).
- International Committee on Taxonomy of Viruses (ICTV): Complete Coronavirus Genome Sequences. 2019, abgerufen am 1. Februar 2020.
- Ben Hu, Lei-Ping Zeng, Xing-Lou Yang, Xing-Yi Ge, Wei Zhang et al.: Discovery of a rich gene pool of bat SARS-related coronaviruses provides new insights into the origin of SARS coronavirus, in: PLOS Pathogens, 30. November 2017, doi:10.1371/journal.ppat.1006698
- Stefan Hintsche: System der Lebewesen: Rhinolophidae (2013)
- Hufeisennasenfledermäuse. Schutzgemeinschaft Deutscher Wald, Oberursel vom 16. Dezember 2015
- Peng Zhou, Xing-Lou Yang, Xian-Guang Wang, Ben Hu, Lei Zhang, Wei Zhang, Hao-Rui Si, Yan Zhu, Bei Li, Chao-Lin Huang, Hui-Dong Chen, Jing Chen, Yun Luo, Hua Guo, Ren-Di Jiang, Mei-Qin Liu, Ying Chen, Xu-Rui Shen, Xi Wang, Xiao-Shuang Zheng, Kai Zhao, Quan-Jiao Chen, Fei Deng, Lin-Lin Liu, Bing Yan, Fa-Xian Zhan, Yan-Yi Wang, Geng-Fu Xiao, Zheng-Li Shi: A pneumonia outbreak associated with a new coronavirus of probable bat origin. In: Nature. 3. Februar 2020, doi:10.1038/s41586-020-2012-7 (englisch, dieser Artikel wurde am 23. Januar 2020 vorab ohne Peer-Review auf bioRxiv veröffentlicht).
- Chengxin Zhang et al.: Protein Structure and Sequence Reanalysis of 2019-nCoV Genome Refutes Snakes as Its Intermediate Host and the Unique Similarity between Its Spike Protein Insertions and HIV-1, in: American Chemical Society: J. Proteome Res. Vom 22. März 2020, doi:10.1021/acs.jproteome.0c00129; PrePrint, PrePrint Volltext (PDF) vom 8. Februar 2020
- Taxonomy Browser Severe acute respiratory syndrome-related coronavirus. In: Website National Center for Biotechnology Information (NCBI). Abgerufen am 7. Februar 2020.
- Roujian Lu, Xiang Zhao, Juan Li, Peihua Niu, Bo Yang, Honglong Wu, Wenling Wang, Hao Song, Baoying Huang, Na Zhu, Yuhai Bi, Xuejun Ma, Faxian Zhan, Liang Wang, Tao Hu, Hong Zhou, Zhenhong Hu, Weimin Zhou, Li Zhao, Jing Chen, Yao Meng, Ji Wang, Yang Lin, Jianying Yuan, Zhihao Xie, Jinmin Ma, William J Liu, Dayan Wang, Wenbo Xu, Edward C Holmes, George F Gao, Guizhen Wu, Weijun Chen, Weifeng Shi, Wenjie Tan: Genomic characterisation and epidemiology of 2019 novel coronavirus: implications for virus origins and receptor binding. In: The Lancet. 29. Januar 2020, doi:10.1016/S0140-6736(20)30251-8.
- Jasper Fuk-Woo Chan, Shuofeng Yuan, Kin-Hang Kok, Kelvin Kai-Wang To, Hin Chu, Jin Yang, Fanfan Xing, Jieling Liu, Cyril Chik-Yan Yip, Rosana Wing-Shan Poon, Hoi-Wah Tsoi, Simon Kam-Fai Lo, Kwok-Hung Chan, Vincent Kwok-Man Poon, Wan-Mui Chan, Jonathan Daniel Ip, Jian-Piao Cai, Vincent Chi-Chung Cheng, Honglin Chen, Christopher Kim-Ming Hui, Kwok-Yung Yuen: A familial cluster of pneumonia associated with the 2019 novel coronavirus indicating person-to-person transmission: a study of a family cluster. In: The Lancet. 24. Januar 2020, doi:10.1016/S0140-6736(20)30154-9.
- Antonio C. P. Wong, Xin Li, Susanna K. P. Lau, Patrick C. Y. Woo: Global Epidemiology of Bat Coronaviruses. In: Viruses. Band 11, Nr. 2, Februar 2019, S. 174, doi:10.3390/v11020174, PMID 30791586, PMC 6409556 (freier Volltext).
- International Committee on Taxonomy of Viruses (ICTV): Virus Taxonomy: 2018b Release. Februar 2019, abgerufen am 1. Februar 2020.
- Taxonomy Browser Betacoronavirus. In: Website National Center for Biotechnology Information (NCBI). Abgerufen am 7. Februar 2020 (im Taxonomy Browser gibt es Weblinks zur Genom- bzw. Nukleotid-Datenbank).