Most recent common ancestor
Most Recent Common Ancestor oder Last Common Ancestor (englisch für letzter gemeinsamer Vorfahr oder auch jüngster gemeinsamer Vorfahr), abgekürzt MRCA bzw. LCA, ist ein Fachausdruck aus den Biowissenschaften, der im Zusammenhang mit der Erforschung der Verwandtschaftsbeziehungen von Individuen oder Taxa gebraucht wird.
Phylogenetik
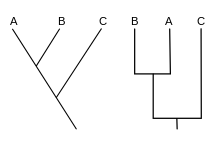
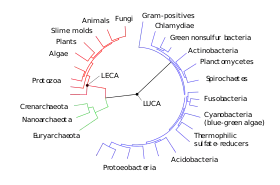
In der kladistisch geprägten Phylogenetik bezieht sich Most Recent Common Ancestor auf den letzten gemeinsamen Vorfahr von zwei Schwestergruppen (Adelphotaxa). Vorfahr steht hier nicht im Wortsinn für ein Individuum, sondern für ein hypothetisches Taxon im Artrang, die sogenannte Stammart*. In einem Kladogramm entspricht eine Stammart dem Punkt, meist Knoten genannt, in dem sich eine Stammlinie (Entwicklungslinie) durch ein Artbildungsereignis in zwei Schwesterlinien aufteilt (dichotome Verzweigung **). Ein Taxon, dessen Untertaxa sich alle auf einen MRCA zurückführen lassen, ist monophyletisch bzw. bildet eine Klade. In der kladistisch geprägten, modernen biologischen Systematik werden prinzipiell nur solche Taxa als gültig anerkannt. Ein Taxon, dessen Untertaxa hingegen keinen MRCA haben, ist para- oder polyphyletisch. Spezialfälle des MRCA im kladistischen Sinn sind der last universal common ancestor (Urvorfahr, wörtlich: letzter universeller gemeinsamer Vorfahr), abgekürzt LUCA, und der Last eukaryotic common ancestor[1] (wörtlich: letzter eukaryotischer gemeinsamer Vorfahr), abgekürzt LECA. LUCA ist die Stammart aller heutigen Lebewesen (Prokaryoten, Protisten, Pilze, Pflanzen und Tiere), sowie wahrscheinlich aller ausgestorbenen mehrzelligen Organismen. Er war eine primitive Mikrobenart, den Bakterien oder einer noch ursprünglichen Form von Leben (vgl. Ribozyt) zugehörig, und die ersten beiden aus ihm hervorgegangenen Arten waren ebenfalls Mikroben. LECA ist hingegen die evolutionsgeschichtlich deutlich jüngere Stammart aller Organismen mit komplexen Zellen, die einen „echten“ Zellkern, umrandet von einem Zellkernmembran besitzen, das heißt, er steht an der Basis jenes Teils des „Baums des Lebens“, der keine Prokaryoten enthält.
Kladogramme sind die übliche Darstellungsform der Ergebnisse einer kladistischen Verwandtschaftsanalyse, die heute in der Regel mit Hilfe eines speziell dafür entwickelten Computerprogrammes durchgeführt wird. Die dafür nötige Datenbasis kann sowohl durch die Erfassung morphologischer Merkmale und deren Merkmalszuständen als auch durch die Untersuchung des Erbgutes (meist einzelne, ausgewählte Gene oder DNA-Sequenzen der nuklearen oder mitochondrialen DNA) exemplarischer Vertreter jener Arten gewonnen werden, deren Verwandtschaft erforscht werden soll. Im resultierenden Kladogramm kann dann leicht abgelesen werden, welche Arten und übergeordneten Taxa auf einen jüngsten gemeinsamen Vorfahren zurückgehen und welche nicht. So lassen sich unter anderem Aussagen darüber anstellen, ob ein bestimmtes Merkmal, das bei mehreren verschiedenen Arten vorkommt, von einem MRCA übernommen wurde, es damit homolog ist, oder ob es bei einer, mehreren oder sogar bei allen der untersuchten Arten jeweils unabhängig – konvergent – entstanden ist. Zudem weist bei morphologisch basierten Analysen jeder Knoten eine bestimmte Kombination von Merkmalszuständen auf, wobei es sich um die für die jeweilige Klade ursprünglichen (anzestrale) Merkmalszustände handelt. Diese entsprechen den Merkmalszuständen beim MRCA dieser Klade. Analog dazu liefern genbasierte Analysen die jeweils anzestralen Basenpaarkonfigurationen der untersuchten DNA-Sequenz für eine Klade. Darüber hinaus können, fußend auf anderweitig ermittelten phylogenetischen Hypothesen, mithilfe spezieller Computerprogramme aus einem Datensatz von DNA-Sequenzen, die ein bestimmtes Protein codieren, anzestrale Zustände dieses Gens rekonstruiert werden. Nachfolgend können die entsprechenden anzestralen Proteine in vitro synthetisiert (exprimiert) und diese schließlich auf ihre Eigenschaften untersucht werden.[2]
Mit Hilfe der molekularen Uhr kann aus einem molekulargenetischen Datensatz der Zeitpunkt§ in der Vergangenheit ermittelt werden, an dem sich zwei Entwicklungslinien getrennt haben (englisch: divergence date), das heißt, der Zeitpunkt, an dem die gemeinsame Stammart einer bestimmten Klade sich in zwei neue Arten aufspaltete. Bei Ermittlung der Divergenzzeitpunkte möglichst vieler Unterkladen in einer Klade können so der zeitliche Verlauf von adaptiven Radiationen in dieser Klade bestimmt und Rückschlüsse auf Verbreitungswege (d. h. die Paläobiogeographie) gezogen werden.[3]
Populationsgenetik und Genetische Genealogie
In der Populationsgenetik bezieht sich Most Recent Common Ancestor auf ein Individuum, das der letzte gemeinsame Vorfahr einer heute lebenden Gruppe von Individuen ist. Im gleichen Sinn wird die Bezeichnung auch in der Genetischen Genealogie verwendet, wobei sich in dieser Disziplin die Untersuchungen weitgehend auf Menschen beschränken.
In Populationsgenetik und Genetischer Genealogie wird der MCRA meist über DNA-Sequenzen des Y-Chromosoms oder mitochondrialer DNA ermittelt.[4] Genauer gesagt, wird, ähnlich wie bei kladistischen Analysen auf molekularer Basis, aus den genetischen Daten einer geeigneten Stichprobe mittels eines Algorithmus für die betreffende DNA-Sequenz die Basenpaarkonfiguration des MRCA dieser Stichprobe rekonstruiert. Auf dieser Grundlage lässt sich anschließend zum Beispiel ermitteln, in welcher heute existenten Population die genetische Übereinstimmung mit diesem MRCA am größten ist. Die geographische Region, in der die Population mit der größten Übereinstimmung lebt, kann dann als die wahrscheinliche Herkunftsregion des MRCA betrachtet werden. So lässt sich u. a. herausfinden, in welchen Refugien heute in Europa weit verbreitete Arten die letzte Eiszeit überlebt haben.[5] Auch die sogenannte Out-of-Africa-II-Theorie über die Herkunft und Verbreitung des modernen Menschen (Homo sapiens) wird von den Ergebnissen einer vergleichenden Untersuchung von DNA-Sequenzen menschlicher mitochondrialer DNA gestützt (siehe auch Mitochondriale Eva).
Zudem kann die rekonstruierte Basenpaarkonfiguration eines MRCA auch in der Populationsgenetik und der genetischen Genealogie als Grundlage für den Einsatz der molekularen Uhr herhalten, mit deren Hilfe ermittelt werden kann, wann in der Vergangenheit der betreffende MRCA gelebt hat.[4]
Anmerkungen
- * Richard Dawkins benutzt in seinem populärwissenschaftlichen Buch The Ancestor’s Tale, das eine Reise entlang der menschlichen Stammlinie beschreibt, für die MRCAs der verschieden inklusiven Kladen, denen der Mensch angehört (Primaten, Säugetiere, Amnioten usw.), den Ausdruck concestor (in der deutschen Version als „Mitfahre“ übersetzt).[6]
- ** in der Kladistik spaltet sich eine Stammart per Konvention stets in zwei neue Arten auf
- § Das Wort „Zeitpunkt“ steht in diesem Zusammenhang genaugenommen für einen Zeitraum, da, in menschlichen Zeitmaßstäben betrachtet, die Artbildung eher ein über mehrere Generationen andauernder Prozess als ein einzelnes Ereignis ist. Ins Verhältnis gesetzt zu den großen Zeitspannen in der Erdgeschichte und in der Evolutionsgeschichte einer relativ inklusiven Klade, kann aber dieser Zeitraum als Zeitpunkt und die Artbildung als Einzelereignis aufgefasst werden.
Einzelnachweise
- Joran Martijn, Thijs J. G. Ettema: From archaeon to eukaryote: the evolutionary dark ages of the eukaryotic cell. Biochemical Society Transactions. Bd. 41, Nr. 1, 2013, S. 451–457, doi:10.1042/BST20120292
- z. B. das anzestrale Rhodopsin der Amnioten, Säugetiere (Mammalia) und höheren Säugetiere (Theria), siehe Constanze Bickelmann, James M. Morrow, Jing Du, Ryan K. Schott, Ilke van Hazel, Steve Lim, Johannes Müller, Belinda S. W. Chang: The molecular origin and evolution of dim-light vision in mammals. Evolution. Bd. 69, Nr. 11, 2015, S. 2995–3003, doi:10.1111/evo.12794; siehe auch Constanze Bickelmann: Visual pigment evolution and the paleobiology of early mammals. Dissertation zur Erlangung des akademischen Grades doctor rerum naturalium (Dr. rer. nat.) im Fach Biologie, Mathematisch-Naturwissenschaftliche Fakultät der Humboldt-Universität zu Berlin, 2011, urn:nbn:de:kobv:11-100191633
- siehe z. B. eine Arbeit über die Phylogenie der Pflanzenfamilie Rapateaceae: T. J. Givnish, T. M. Evans, M. L. Zjhra, T. B. Patterson, P. E. Berry, K. J. Sytsma: Molecular evolution, adaptive radiation, and geographic diversification in the amphiatlantic family Rapateaceae: evidence from ndhF sequences and morphology. Evolution. Bd. 54, Nr. 6, 2000, S. 1915–1937, doi:10.1111/j.0014-3820.2000.tb01237.x
- Bruce Walsh: Estimating the time to the most recent common ancestor for the Y chromosome or mitochondrial DNA for a pair of individuals. Genetics. Bd. 158, Nr. 2, 2001, S. 897–912 (PDF).
- zum Beispiel der Buchfink, siehe Cortland K. Griswold, Allan J. Baker: Time to the most recent common ancestor and divergence times of populations of common chaffinches (Fringilla coelebs) in Europe and North Africa: insights into Pleistocene refugia and current levels of migration. Evolution. Bd. 56, Nr. 1, 2002, S. 143–153, doi:10.1111/j.0014-3820.2002.tb00856.x.
- Richard Dawkins: Geschichten vom Ursprung des Lebens. Ullstein, Berlin 2008, Fußnote S. 22, ISBN 978-3-550-08748-6